Biomedizin: viele Bilder – weniger Rätsel
Der Status Quo: zeitaufwändige und fehleranfällige Analysen
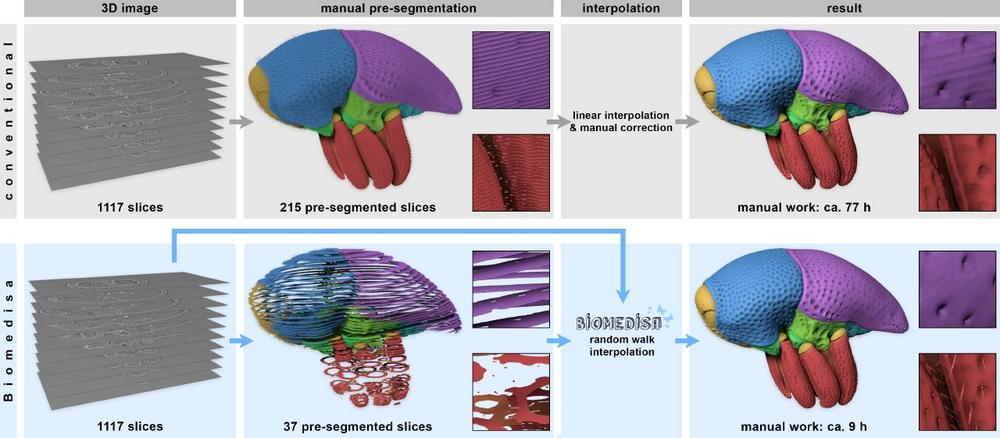
Damit diese umfangreichen Aufnahmen ihr Informationspotential entfalten, bedarf es sehr häufig einer manuellen Segmentierung. Dabei wird ein digitales Bild in verschiedene Schichten aufgeteilt, um die Bildinformationen leichter zu erkennen und auszuwerten. Hierfür werden die erkennbaren Strukturen in eng beieinander liegenden Schichten als sogenannte Labels, wie z.B. „Hintergrund” oder „Objekt”, benannt. Bei der darauffolgenden Interpolation werden die Zwischenräume auf Grundlage der manuell vorsegmentierten Schichten bestimmt. Dabei werden die zugrundeliegenden Bilddaten normalerweise nicht berücksichtigt, wodurch lediglich ein Bruchteil der zur Verfügung stehenden Information verwendet wird.
„Die manuelle Segmentierung unbekannter biomedizinischer Datensätze ist oft sehr zeitaufwändig und fehleranfällig, da sehr viele Schichten segmentiert werden müssen. Zur Analyse dreidimensionaler Bilddaten wird dieses Verfahren aber noch sehr häufig angewendet. In vielen Instituten ist es tatsächlich gang und gäbe, Heerscharen von speziell geschulten Studierenden extra für diese Aufgabe einzusetzen,” so Philipp Lösel aus der Forschungsgruppe „Data Mining and Uncertainty Quantification” (DMQ) am HITS, der Biomedisa entwickelt hat.
Biomedisa: schneller, nutzerfreundlich und genauer
Die Biomedical Image Segmentation App Biomedisa (https://biomedisa.org) ist eine frei verfügbare und leicht zu bedienende Open-Source Online-Anwendung, die speziell für die halbautomatische Segmentierung entwickelt wurde. Die Segmentierung basiert dabei auf einer intelligenten Interpolation einiger weniger vorsegmentierter Schichten, wobei die zugrundeliegenden Bilddaten vollständig mit einbezogen werden. Dadurch können wesentlich größere Abstände zwischen den Schichten gelassen werden. „Biomedisa kann den Segmentierungsprozess enorm beschleunigen und liefert gleichzeitig genauere Ergebnisse als dies bei einer rein manuellen Segmentierung der Fall ist,” so Thomas van de Kamp, Biologe am KIT, der aus eigener Erfahrung weiß, wie mühevoll eine manuelle Bildsegmentierung sein kann. Er steuerte für das Projekt Mikro-CT-Daten bei und evaluierte Biomedisa während des Entwicklungsprozesses.
Die Plattform ist über einen Webbrowser zugänglich (https://biomedisa.org), eine komplexe und langwierige Konfiguration der Software oder der Modellparameter ist nicht erforderlich. Die One-Button-Lösung kann bei verschiedenen 3D-Bildgebungsverfahren und zahlreichen biomedizinischen Anwendungen eingesetzt werden.
„Unser ausdrückliches Ziel war es,” so Vincent Heuveline, Direktor des Universitätsrechenzentrums Heidelberg (URZ) und DMQ-Gruppenleiter am HITS, „ein breit einsetzbares und nutzerfreundliches Tool zu entwickeln, um die Segmentierung von Proben unbekannter Morphologie zu beschleunigen und dabei gleichzeitig die Ergebnisse zu verbessern.”
„Biomedisa ist eine Software, die in direktem Maße von den neuesten Entwicklungen auf dem Gebiet der GPU-Technologie (Graphics Processing Unit) profitiert. Sie wurde speziell für die Verwendung von Graphikbeschleunigern entwickelt, um die stetig zunehmende Menge an Bilddaten zu verarbeiten,” fasst Philipp Lösel zusammen.
Auf dem Weg zu einer vollautomatischen Segmentierung
Daneben bietet Biomedisa noch eine Vielzahl weiterer Funktionen, wie z.B. die Entfernung von Ausreißern oder das Füllen von Löchern. Oberflächen können geglättet und die Unsicherheit, mit der die Ergebnisse erzielt wurden, quantifiziert werden. Außerdem können die Daten mit einer 3D-Rendering-Software visualisiert und mit anderen geteilt werden.
Zu guter Letzt ermöglicht Biomedisa das Training künstlicher neuronaler Netze. Dieses Verfahren gestattet eine vollständig automatisierte Segmentierung, falls eine Vielzahl ähnlicher Strukturen segmentiert wird, wie dies z.B. beim menschlichen Herzen der Fall ist. Dadurch werden numerische Simulationen möglich, die auf einem patientenspezifischen Modell des Herzens basieren und Ärztinnen und Ärzte im Krankenhaus bei der Planung chirurgischer Eingriffe unterstützen sollen.
Die Kombination all dieser Eigenschaften machen Biomedisa zu einer idealen Plattform für alle, denen Bilder im Idealfall mehr als tausend Worte sagen sollen.
Die Arbeit fand im Rahmen eines interdisziplinären Forschungsprojektes mit Wissenschaftler/-innen der Universität Heidelberg, dem Karlsruher Institut für Technologie (KIT) und der Technischen Universität Darmstadt statt. Die Ergebnisse , die sich vor allem an Forschende ohne fundierte Computerkenntnisse richten, wurden jetzt in der Fachzeitschrift Nature Communications veröffentlicht.
Philipp D. Lösel, Thomas van de Kamp, Alejandra Jayme, Alexey Ershov, Tomáš Faragó, Olaf Pichler, Nicholas Tan Jerome, Narendar Aadepu, Sabine Bremer, Suren A. Chilingaryan, Michael Heethoff, Andreas Kopmann, Janes Odar, Sebastian Schmelzle, Marcus Zuber, Joachim Wittbrodt, Tilo Baumbach & Vincent Heuveline: Introducing Biomedisa as an open-source online platform for biomedical image segmentation. Nature Communications, 4 November 2020. DOI 10.1038/s41467-020-19303-w
https://www.nature.com/articles/s41467-020-19303-w
Biomedisa Tutorials auf YouTube
https://www.youtube.com/channel/UCTNOthYVKyIWVvYYZSU_mfQ
Das Heidelberger Institut für Theoretische Studien (HITS) wurde 2010 von SAP-Mitbegründer Klaus Tschira (1940-2015) und der Klaus Tschira Stiftung als private, gemeinnützige Forschungseinrichtung ins Leben gerufen.
Das HITS betreibt Grundlagenforschung in den Naturwissenschaften, der Mathematik und der Informatik, dabei werden große, komplexe Datenmengen verarbeitet, strukturiert und analysiert und computergestützte Methoden und Software entwickelt. Die Forschungsfelder reichen von der Molekularbiologie bis zur Astrophysik.
www.h-its.org
HITS gGmbH
Schloss-Wolfsbrunnenweg 35
69118 Heidelberg
Telefon: +49 (6221) 533-245
Telefax: +49 (6221) 533-198
http://www.h-its.org
Wissenschaftlicher Kontakt
Telefon: +49 (6221) 533-520
E-Mail: Philipp.Loesel@h-its.org
Leiter
Telefon: +49 (6221) 533245
Fax: +49 (6221) 533298
E-Mail: peter.saueressig@h-its.org
![]()